Das Unsichtbare im Erbgut finden
Forscher entwickeln ein Verfahren, um Sequenzierungsdaten mehr Informationen zu entlocken
Höhere Lebewesen speichern ihr Erbgut im Zellkern als Desoxyribonukleinsäure oder DNA. Einzelne Abschnitte, die Gene, werden bei der Transkription in Ribonukleinsäuren, sogenannte mRNAs, umgewandelt. Daraus entstehen bei der Translation Proteine als wichtigste Funktionseinheiten.
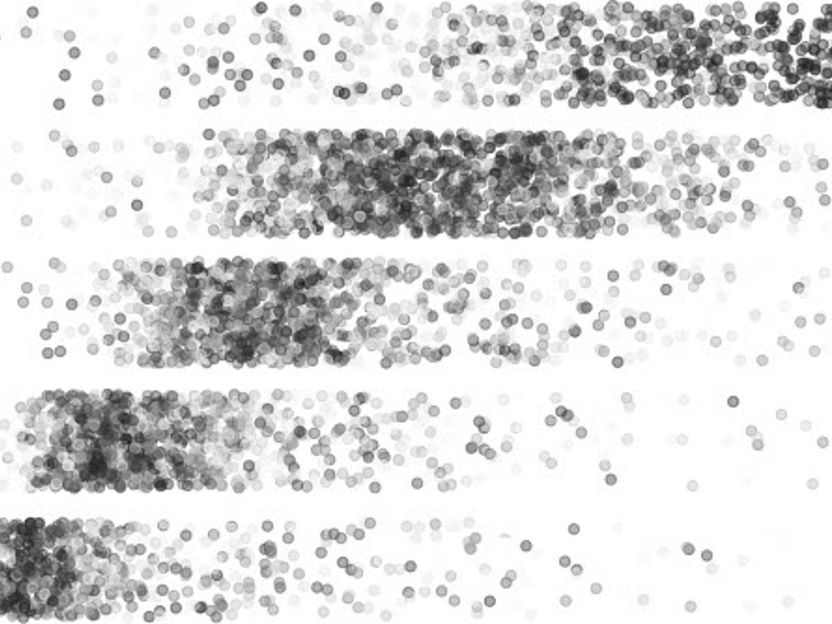
Punkte repräsentieren RNA-Moleküle, die abhängig von ihrer Größe verschieden weit im elektrischen Feld wandern. Größere Moleküle (rechts) werden in Ladder-seq von kleineren Molekülen (links) wie auf den Stufen einer Leiter getrennt.
LMU
Zellen können unterschiedliche Gene an- oder abschalten. Auch bei Krankheiten finden sich charakteristische Muster der Genexpression. Deshalb versuchen Wissenschaftlerinnen und Wissenschaftler, mRNA-Moleküle zu sequenzieren, um ihnen weitere Informationen zu entlocken. Nur gingen bei etablierten Technologien oft Informationen verloren.
Ein Team um Dr. Stefan Canzar vom Genzentrum der LMU stellt in Nature Biotechnology jetzt Ladder-seq vor: ein Verfahren, das zu besseren Ergebnissen führt. Die Wissenschaftlerinnen und Wissenschaftler kombinieren Änderungen im Sequenzierungsprotokoll mit rechnergestützten Verfahren. Mit den zusätzlichen Informationen kann Canzars Team beispielsweise die Funktion regulatorischer Einheiten bei neuralen Stammzellen im Gehirn von Mäusen entschlüsseln.
Ein Puzzle mit zusätzlichen Informationen
„Bislang werden bei der Sequenzierung im ersten Schritt mRNA-Moleküle zerkleinert, was bildlich gesprochen zu Puzzleteilchen führt“, erklärt Canzar. Diese Fragmente sequenzieren moderne Geräte dann parallel, was Zeit spart. Mit leistungsfähigen Rechnern werden einzelne Teile der Sequenz wieder zusammengesetzt. In den letzten zehn bis 15 Jahren wurden etliche Methoden weiter optimiert. „Dennoch wissen wir, dass bei dem Vorgang Informationen verlorengehen, die nicht wieder rekonstruierbar ist“, so der LMU-Forscher.
Dr. Francisca Rojas Ringeling und Shounak Chakraborty aus Canzars Gruppe haben das übliche Protokoll verändert. Vor der eigentlichen Sequenzierung trennen Forschende RNA-Moleküle anhand ihrer Länge auf. Das gelingt am einfachsten per Elektrophorese, einer Technologie zur Separation im elektrischen Feld. Unterschiedlich große mRNAs wandern verschieden weit. Im Gel erscheinen sie als Leiter, daher der Name Ladder-seq. Erst dann folgen die Fragmentierung und die Sequenzierung. Algorithmen nutzen Information zur Größe, um einzelne Puzzleteilchen präziser als bislang möglich zusammenzusetzen.
Anwendungsbeispiel aus der Neurobiologie
Die LMU-Forschenden zeigen anhand eines Anwendungsbeispiels, was Ladder-seq leisten kann. Im Experiment haben sie sich mit dem alternativen Spleißen im sich entwicklenden Maushirn befasst. Entfernt man eine chemische Modifikation der RNA, verändert sich die Sequenz des RNA-Moleküls selbst. Sprich: Man beobachtet alternatives Spleißen. Aus dem gleichen Gen entsteht eine andere mRNA – und folglich ein anderes Protein, dem bestimmte strukturelle Bereiche fehlen. Sie erfüllen ihre biologischen Aufgaben im Gehirn von Mäusen nicht mehr. Neurale Stammzellen bleiben in diesem Entwicklungsstadium. Sie differenzieren sich nicht mehr zu Nervenzellen, weil entsprechende Gene fehlreguliert sind. Das Gehirn betroffener Nager ist stark deformiert; sie sterben bald nach der Geburt. „Ohne die neue Methode hätten wir solche Fragen nie so differenziert beantworten können“, erklärt Canzar.
Originalveröffentlichung
Francisca Rojas Ringeling, Shounak Chakraborty, Caroline Vissers, Derek Reiman, Akshay M. Patel, Ki-Heon Lee, Ari Hong, Chan-Woo Park, Tim Reska, Julien Gagneur, Hyeshik Chang, Maria L. Spletter, Ki-Jun Yoon, Guo-li Ming, Hongjun Song, Stefan Canzar; "Partitioning RNAs by length improves transcriptome reconstruction from short-read RNA-seq data"; Nature Biotechnology; 2021
Meistgelesene News
Originalveröffentlichung
Francisca Rojas Ringeling, Shounak Chakraborty, Caroline Vissers, Derek Reiman, Akshay M. Patel, Ki-Heon Lee, Ari Hong, Chan-Woo Park, Tim Reska, Julien Gagneur, Hyeshik Chang, Maria L. Spletter, Ki-Jun Yoon, Guo-li Ming, Hongjun Song, Stefan Canzar; "Partitioning RNAs by length improves transcriptome reconstruction from short-read RNA-seq data"; Nature Biotechnology; 2021
Organisationen
Weitere News aus dem Ressort Wissenschaft

Holen Sie sich die Analytik- und Labortechnik-Branche in Ihren Posteingang
Mit dem Absenden des Formulars willigen Sie ein, dass Ihnen die LUMITOS AG den oder die oben ausgewählten Newsletter per E-Mail zusendet. Ihre Daten werden nicht an Dritte weitergegeben. Die Speicherung und Verarbeitung Ihrer Daten durch die LUMITOS AG erfolgt auf Basis unserer Datenschutzerklärung. LUMITOS darf Sie zum Zwecke der Werbung oder der Markt- und Meinungsforschung per E-Mail kontaktieren. Ihre Einwilligung können Sie jederzeit ohne Angabe von Gründen gegenüber der LUMITOS AG, Ernst-Augustin-Str. 2, 12489 Berlin oder per E-Mail unter widerruf@lumitos.com mit Wirkung für die Zukunft widerrufen. Zudem ist in jeder E-Mail ein Link zur Abbestellung des entsprechenden Newsletters enthalten.






















































