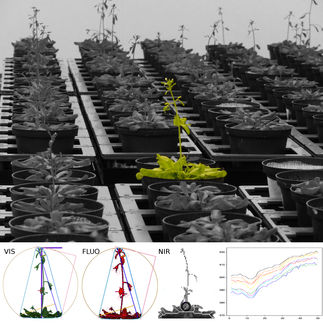
Wissenschaftliche Bildanalyse für jedermann
Neue Software ermöglicht die automatisierte Auswertung von Bilddaten ohne Programmierkenntnisse
Die Software JIPipe wurde von Wissenschaftlern am Leibniz-Institut für Naturstoff-Forschung und Infektionsbiologie (Leibniz-HKI) entwickelt und vereinfacht die Analyse von in der Forschung entstandenen Bildern entscheidend. Nutzer*innen können nach ihrem Anwendungsbedarf Flowcharts erstellen und so ohne Programmierkenntnisse automatische Bildanalysen mithilfe künstlicher Intelligenz durchführen. JIPipe basiert auf ImageJ, einem Standardprogramm zur wissenschaftlichen Auswertung von biomedizinischen Mikroskopaufnahmen. Die Autoren stellen ihre Entwicklung nun in Nature Methods vor.
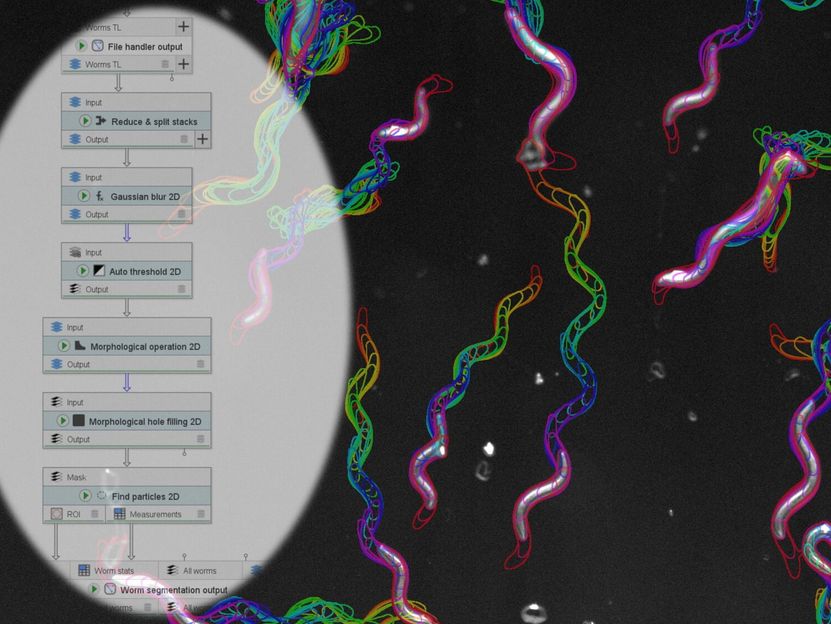
Mit JIPipe lassen sich beispielsweise die Bewegungsprofile von Fadenwürmern analysieren.
Hannah Büttner, Zoltán Cseresnyés, Ruman Gerst
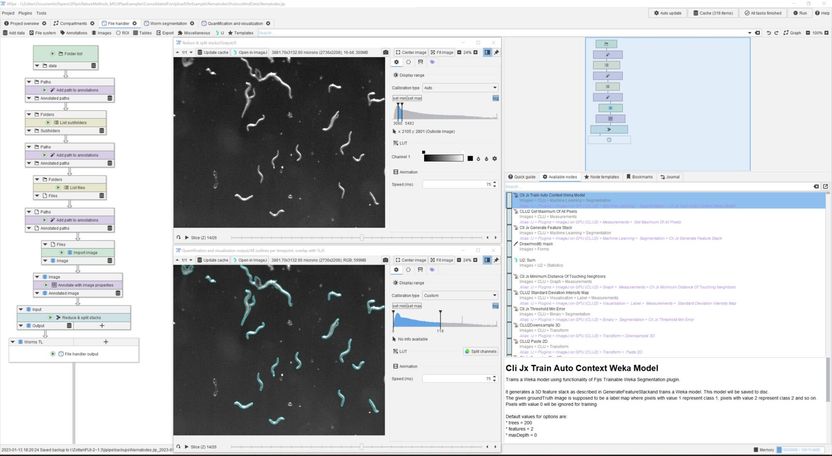
Screenshot einer JIPipe-Analyse zum Überleben von Nematoden.
Zoltán Cseresnyés/Leibniz-HKI
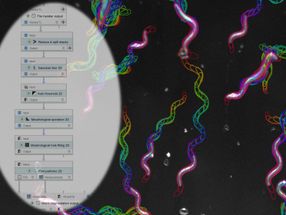
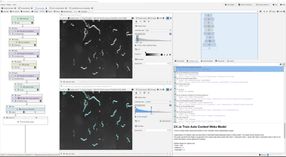
Bilder – vor allem mikroskopische Aufnahmen – spielen in der biomedizinischen Forschung eine große Rolle. Mithilfe von Fluoreszenzmarkierungen werden beispielsweise Vorgänge in Zellen sichtbar gemacht. „Ein Bild sagt mehr als tausend Worte – das ist nach wie vor wahr“, sagt Thilo Figge, Leiter der Forschungsgruppe Angewandte Systembiologie am Leibniz-HKI und Professor an der Friedrich-Schiller-Universität Jena. Doch die Auswertung stellt die Forschenden vor zunehmende Herausforderungen. „Es werden immer höhere Auflösungen und damit größere Datenmengen erzeugt“, erklärt Figge. „Gleichzeitig sind die Methoden der KI, also der künstlichen Intelligenz, mittlerweile so weit entwickelt, dass sie für Forschende ohne Programmierkenntnisse immer schwieriger anzuwenden sind.“
Das nun am Leibniz-HKI entwickelte Open Source Programm JIPipe – kurz für Java Image Processing Pipeline – soll das vereinfachen. „JIPipe ist ein Werkzeug, das keine Programmierfähigkeiten benötigt“, erklärt Entwickler Ruman Gerst, Mitarbeiter der Forschungsgruppe Angewandte Systembiologie. Stattdessen nutzt die Software eine visuelle Programmiersprache: Mithilfe vorgefertigter Bausteine können Nutzer*innen individuelle Arbeitsabläufe erstellen, um so Bilder nach ihren spezifischen Anforderungen automatisiert zu analysieren.
JIPipe unterstützt weitere Programmiersprachen
Das Programm basiert auf der Open Source Software ImageJ, die sich als Standard in der wissenschaftlichen Bildanalyse etabliert hat. JIPipe und ImageJ sind vollständig miteinander kompatibel und ergänzen einander bei der wissenschaftlichen Bildanalyse. „Unser Programm unterstützt ImageJ Skripte und enthält die üblichen Funktionen und Macros“, erklärt Gerst. Auch andere Programmiersprachen wie Python und R werden unterstützt.
Das Vorläuferprogramm wurde von Zoltán Cseresnyés, ebenfalls Mitarbeiter der Forschungsgruppe Angewandte Systembiologie, bereits vor einigen Jahren entwickelt. „Ursprünglich habe ich den Code für einen Phagozytose-Assay geschrieben“, erklärt Cseresnyés. Bei der Phagozytose nimmt eine Zelle ein Partikel – beispielsweise eine andere Zelle – auf und zersetzt es, was üblicherweise mit Fluoreszenzfarbstoffen sichtbar gemacht wird.
Mit der Zeit erweiterte der Spezialist für Bildgebung den Code immer wieder für neue Anwendungsfälle – das Programm wurde unübersichtlich und zu komplex. „Uns wurde klar, dass wir das umgestalten und modular aufbauen müssen“, erzählt Cseresnyés, weswegen das Team den Bioinformatiker Ruman Gerst ins Boot holte. Dieser schlug zudem die jetzige visuelle Programmiersprache vor, welche es ermöglicht, die Bilddaten von beliebigen biomedizinischen Problemstellungen zu analysieren.
Reproduzierbare Ergebnisse
JIPipe wurde bereits für mehrere Studien genutzt, beispielsweise um die Effizienz der Medikamentenabgabe durch sogenannte Nanocarrier in der Leber zu untersuchen oder um die Überlebensrate von Fadenwürmern zu testen, die toxinproduzierende Bakterien verdaut haben. Auch Konfrontationen zwischen Immunzellen und Pilzsporen wurden mit dem neuen Programm analysiert. Die Entwickler bieten im Rahmen des Microverse Imaging Center und der Nationalen Forschungsdateninfrastruktur NFDI4BioImage auch Kurse zur Nutzung an. „Im Gegensatz zur manuellen Bildanalyse liefert die automatisierte Analyse immer die gleichen Ergebnisse, ist somit reproduzierbar und entspricht den sogenannten FAIR-Prinzipien für die Bildanalyse“, betont Thilo Figge. Der Begriff FAIR kommt ursprünglich aus dem Bereich des Forschungsdatenmanagements und steht für “Findable (Auffindbar), Accessible (Zugänglich), Interoperable (Interoperabel) und Reusable (Wiederverwendbar)“.