Von der Verwandtschaft lernen
Neues Webtool vereinfacht die Vorhersage von Regelnetzwerken in Bakterien
Raus aus dem Labor, ran an den Rechner: Bioinformatikerinnen und Bioinformatiker aus Freiburg haben ein Computerprogramm entwickelt, mit dem man die Funktion von Genregulatoren in Bakterien vorhersagen kann. Das Programm könnte im Labor viel Arbeit ersparen. Die Online-Software CopraRNA kann mit großer Genauigkeit ermitteln, welche Gene in Bakterien von bestimmten Regulatoren gesteuert werden.

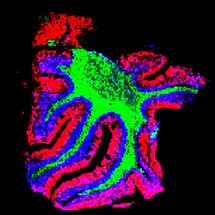
Webserver-Darstellung der vorhergesagten Interaktionsstellen in einer nicht-kodierenden RNA
© Jens Georg
Die Forscherinnen und Forscher der Arbeitsgruppen für Genetik und experimentelle Bioinformatik von Prof. Dr. Wolfgang Hess und für Bioinformatik von Prof. Dr. Rolf Backofen, Mitglied des Exzellenzclusters BIOSS Centre for Biological Signalling Studies, haben in Zusammenarbeit mit der Arbeitsgruppe von Prof. Dr. Jörg Vogel, Universität Würzburg, viele verwandte Bakterien in ihren Regulationsmechanismen verglichen. Erst dieser Vergleich erlaubt es dem neu entwickelten Computerprogramm CopraRNA, aus mehr als 4.000 Genen diejenigen herauszufiltern, die von einem Regulator angesteuert werden. Das Programm macht aufwendige Tests im Labor überflüssig und vereinfacht die Suche nach bakteriellen Regulatoren. Wenn man die Funktion dieser Moleküle versteht, kann man sie verwenden, um in der Medizin Erreger zu bekämpfen oder Bakterien in der Biotechnologie nutzbar zu machen.
Im Unterschied zu den meisten Molekülen, die Zellen steuern, sind die untersuchten Regulatoren keine Eiweiße: Es sind RNA-Moleküle. Die Ribonukleinsäure besteht ähnlich der DNA aus einem Vierercode von Nukleinbasen, die mit einem Zucker- und Phosphatrückgrat eine Kette bilden. Bisher war die RNA als Arbeitskopie der DNA für die Proteinsynthese bekannt. Aus den hier vorgestellten RNA-Molekülen werden keine Proteine hergestellt. Sie heißen daher nicht-kodierende RNA-Moleküle oder ncRNA. Seit kurzem weiß man: Diese Moleküle spielen eine wichtige Rolle im Signalnetzwerk der Zelle, zum Beispiel wenn das Bakterium auf äußere Einflüsse reagiert. Als Regulator bindet die RNA an viele verschiedene Gene der Bakterienzelle und steuert so die Synthese von Proteinen.
Tausende neu entdeckte ncRNA Regulatoren stellen eine neue Art Steuerungswerkzeug in der Bakterienzelle dar. Ihre Funktion zu erkunden ist im Labor mühsam: Viele umfangreiche Tests sind notwendig, um Gensequenzen zu bestimmen, mit denen sie in Kontakt treten. Einfacher ist es, wenn man die Moleküle so versteht, dass man anhand ihrer Struktur vorhersagen kann, welche Gene sie an- und ausschalten. Zu diesem Zweck haben die Bioinformatiker im Rahmen des vom Bundesministerium für Bildung und Forschung geförderten Verbundes „ebio: RNAsys – Systembiologie der RNA“ die Software CopraRNA entwickelt. Forscher geben nur die Sequenz der RNA-Kette von mindestens drei Bakterienarten auf der Webseite rna.informatik.uni-freiburg.de/CopraRNA/ ein und erfahren mögliche Funktionen. Ob die Vorhersage zutrifft, muss dann im Labor getestet werden.
Originalveröffentlichung
Meistgelesene News
Weitere News aus dem Ressort Wissenschaft
Diese Produkte könnten Sie interessieren

Limsophy LIMS von AAC Infotray
Optimieren Sie Ihre Laborprozesse mit Limsophy LIMS
Nahtlose Integration und Prozessoptimierung in der Labordatenverwaltung

OMNIS von Metrohm
OMNIS – die Plattform zur Integration der Metrohm Titrando Gerätegeneration
OMNIS ermöglicht die Kombination von Bestandskomponenten mit neuester OMNIS Hard- und Software

LAUDA.LIVE von LAUDA
LAUDA.LIVE - Die digitale Plattform für Ihre Geräteverwaltung
Viefältige Flottenmanagementoptionen für jedes LAUDA Gerät - mit und ohne IoT-Anbindung

Holen Sie sich die Analytik- und Labortechnik-Branche in Ihren Posteingang
Mit dem Absenden des Formulars willigen Sie ein, dass Ihnen die LUMITOS AG den oder die oben ausgewählten Newsletter per E-Mail zusendet. Ihre Daten werden nicht an Dritte weitergegeben. Die Speicherung und Verarbeitung Ihrer Daten durch die LUMITOS AG erfolgt auf Basis unserer Datenschutzerklärung. LUMITOS darf Sie zum Zwecke der Werbung oder der Markt- und Meinungsforschung per E-Mail kontaktieren. Ihre Einwilligung können Sie jederzeit ohne Angabe von Gründen gegenüber der LUMITOS AG, Ernst-Augustin-Str. 2, 12489 Berlin oder per E-Mail unter widerruf@lumitos.com mit Wirkung für die Zukunft widerrufen. Zudem ist in jeder E-Mail ein Link zur Abbestellung des entsprechenden Newsletters enthalten.